Cas9-enriched nanopore sequencing enables comprehensive and multiplexed detection of repeat expansions
Cas9 기반 나노포어 타깃 시퀀싱으로 STR 반복 확장을 한 번에 진단하다
– Nanopore Cas9-targeted sequencing(nCATS)와 STRiker를 이용한 차세대 반복확장 진단 전략
1. 연구 배경: STR 반복 확장 진단의 한계
Short Tandem Repeat(STR)는 2–7 bp 길이의 짧은 서열이 반복되는 구조로, 인간 유전체 전반에 100만 개 이상 존재합니다. 이 중 일부 STR은 반복 횟수가 비정상적으로 증가하면서 소뇌실조(spinocerebellar ataxia), NIID, 근육·신경계 질환 등을 유발합니다. 하지만 기존 STR 진단 방법에는 명확한 한계가 있습니다.
- PCR 기반 fragment analysis
- 반복 길이는 알 수 있지만,
- 반복 서열의 정확한 구조(중단(interruption), motif 변화)는 알 수 없음
- PCR 과정에서 DNA methylation 정보 소실
- Short-read NGS (150–300 bp)
- 반복 확장이 read 길이를 초과하면 정확한 repeat count 불가
- 복잡한 반복 구조(혼합 motif) 분석 불가능
- WES/WGS
- 반복 영역 조립(assembly)이 매우 어려워 정확한 repeat 해석이 힘듦
즉, 반복 길이 + 반복 구조 + 메틸화 정보를 동시에 정확히 분석할 수 있는 방법이 필요했습니다.
2. 핵심 아이디어: nCATS + 나노포어 + STRiker
이 연구는 기존 nCATS(nanopore Cas9-targeted sequencing) 기술을 대폭 개선하고, 여기에 STR 전용 분석 알고리즘 STRiker를 결합했습니다.
핵심 목표는 단 하나다.
“한 번의 검사로, 현재 알려진 모든 STR 반복 확장 질환(56개 locus)을 동시에 정확하게 진단하자.”
3. 전체 워크플로우 개요
(기존 임상 진단: 수 주 ~ 수 개월) |
 |
4. 실험 방법 (Methods)
4.1 STR 타깃 설계 (56개 locus)
|
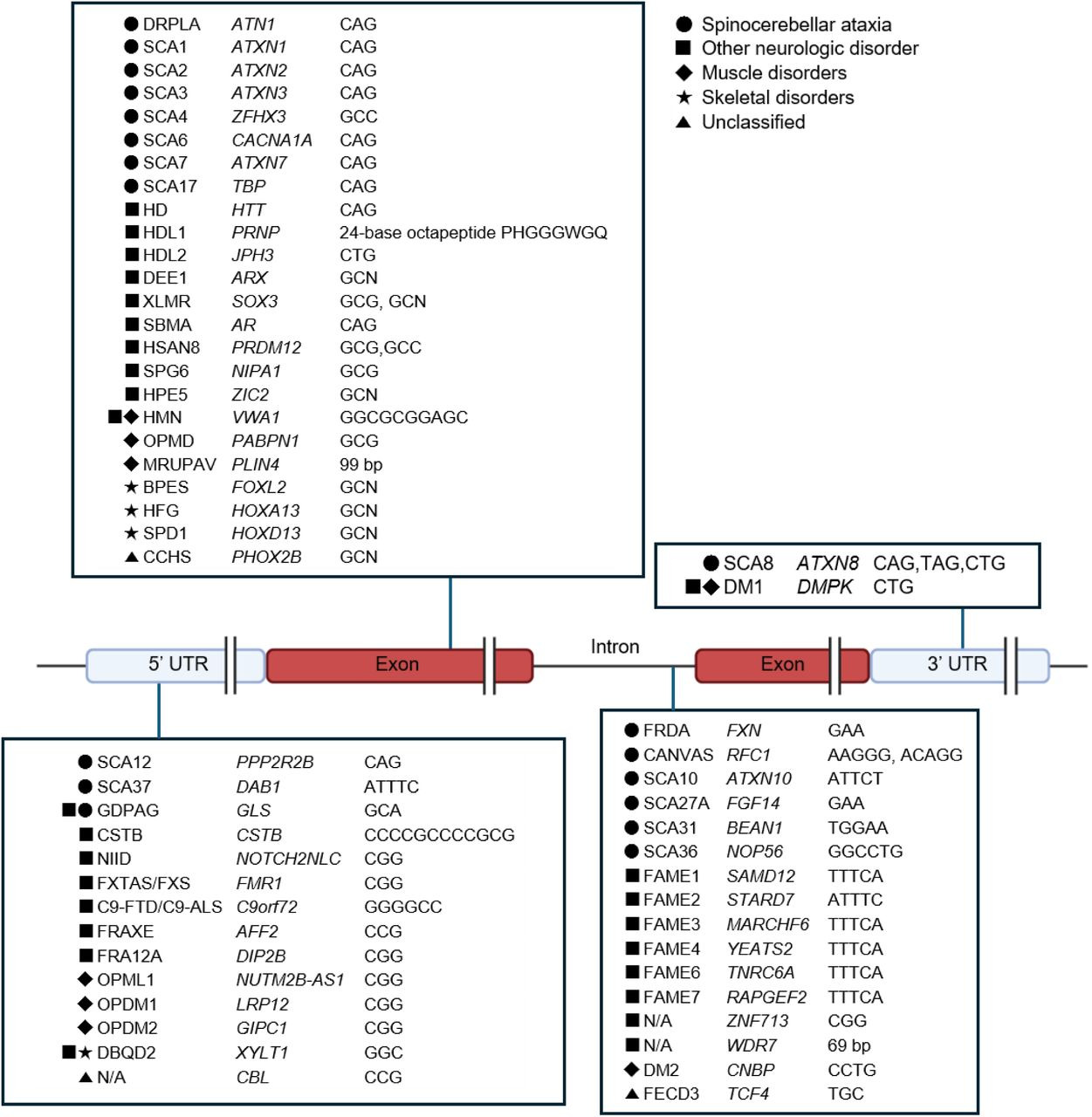 |
4.2 Guide RNA(gRNA) 최적화 (in vitro cleavage assay)
|
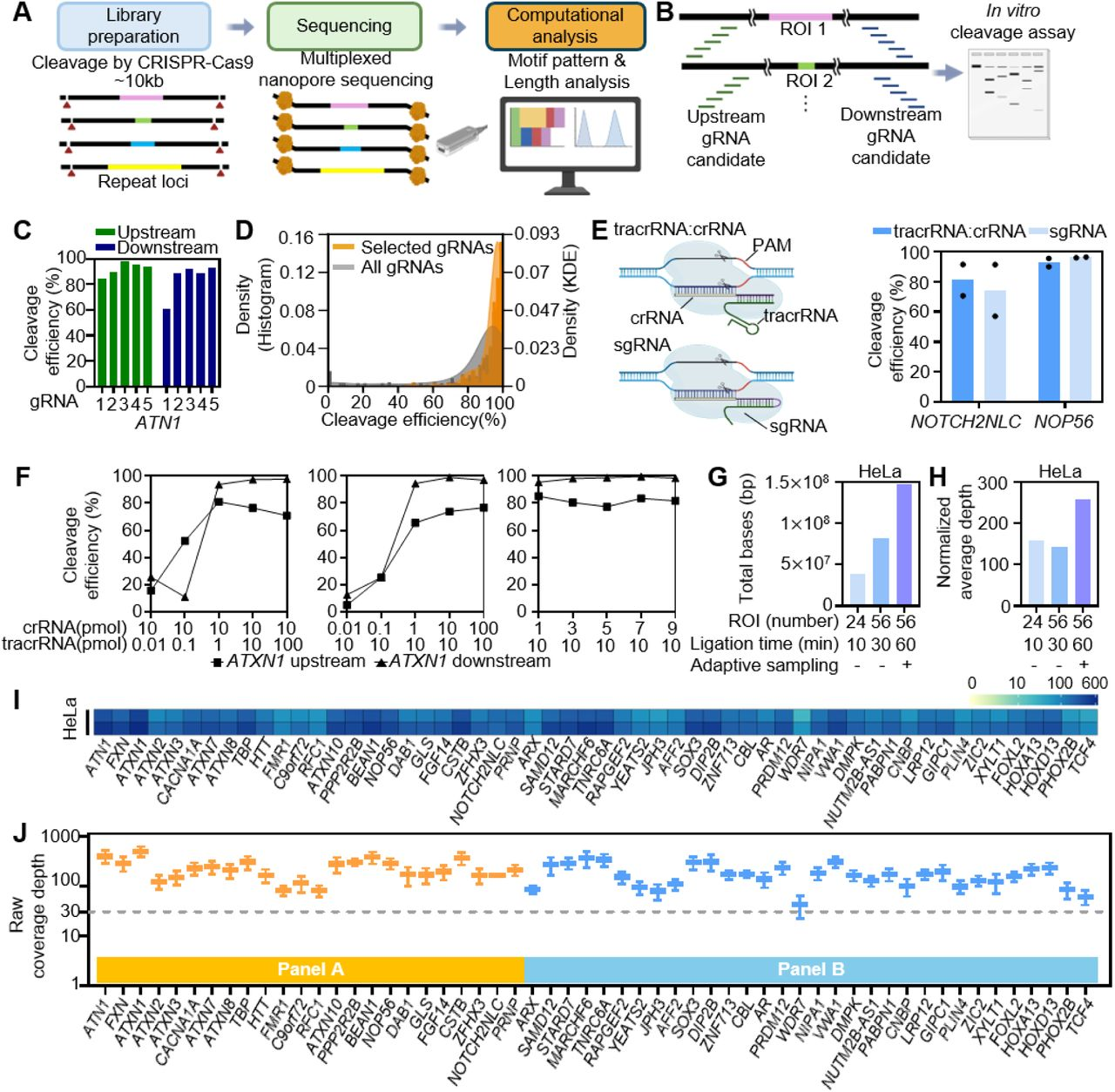 |
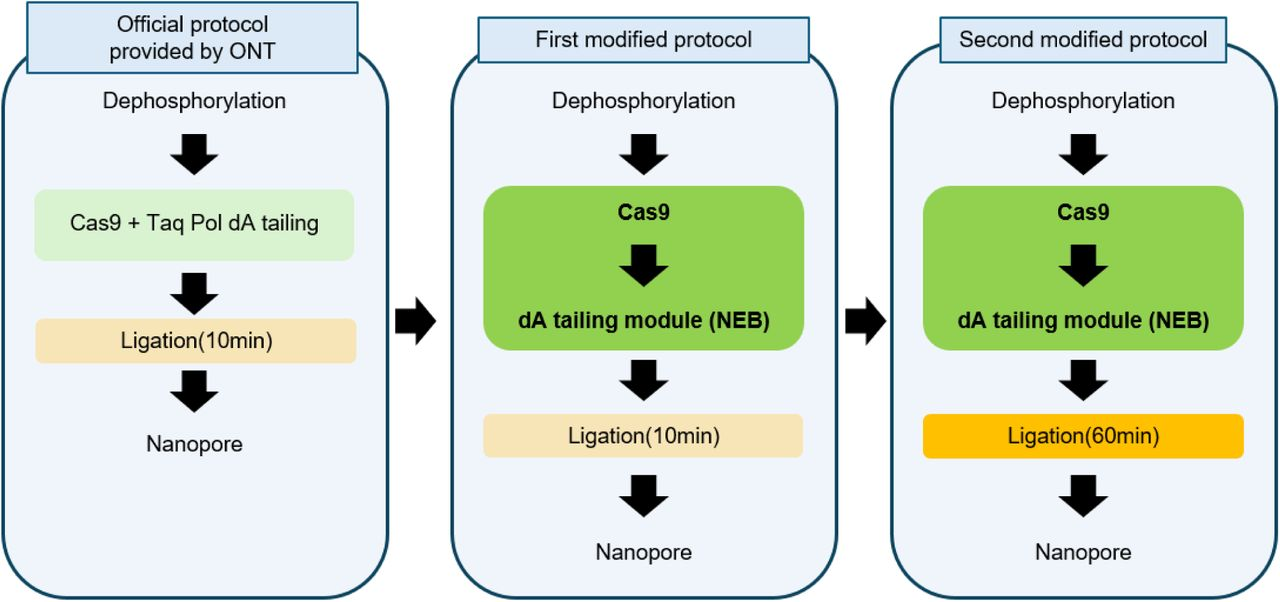
4.3 nCATS 프로토콜 개선 포인트
기존 ONT Cas9 프로토콜 대비 핵심 개선 3가지:
|
 |
4.4 시퀀싱 및 기본 분석
- 플랫폼: MinION + R10.4.1
- Basecalling: Dorado v0.6.2
- Alignment: minimap2
- BAM 처리: samtools
5. STRiker: STR 전용 분석 알고리즘
STRiker는 기존 도구와 달리 “모르는 motif도 찾아내는” 것이 핵심입니다.
5.1 STRiker의 특징
- Reference motif + de novo motif 동시 탐지
- motif 길이: 3–30 bp
- 연속 반복 ≥3회 이상 → STR 후보
- 회전 대칭(motif rotation) 자동 정규화
- 반복 중간의 interruption 패턴 명확히 분해
예시:
(CAG)₃ (CAA)₁ (CAG)₂
5.2 STRiker 출력 결과
- PDF 리포트
- Read별 motif heatmap
- Repeat length 분포(KDE)
- 병적 threshold 시각화
- Excel 파일
- motif 종류별 반복 횟수
- 메틸화 정보(5mC) 동시 제공
임상의가 “눈으로 바로 판단 가능한” 구조
6. 임상 적용 결과 (37명 소뇌실조 환자)
- 기존 검사(WES/WGS/fragment analysis)로 원인 미확인 환자
- nCATS + STRiker 적용 결과:
진단 성과
→ 단일 검사로 진단 종료 |
 |
7. 새롭게 밝혀진 생물학적 인사이트
7.1 FGF14 반복 구조의 다양성
- 기존: GAA, GAAGGA
- 신규 발견:
- AAAAAC
- GCAGAAGCA(GAA)₂
- 특정 motif는 조기 발병·비전형적 증상과 연관
7.2 메틸화와 세대 간 반복 변화 (NOTCH2NLC)
- 나노포어의 장점: native DNA 메틸화 보존
- 흥미로운 관찰:
- 모계 유전 시 반복 수 증가 + hypermethylation
- 반복은 크지만 증상은 억제된 사례 존재
반복 길이 + 메틸화 상태를 동시에 봐야 질병 예측 가능
8. 이 연구의 의미
- PCR 없이 STR 진단 가능
- 반복 길이·구조·메틸화 동시 분석
- 모든 STR 질환을 단일 패널로 진단
- 임상 적용 가능한 속도(1–2일)
이 연구는 STR 반복 확장 질환 진단에서 “WES 이전과 이후”처럼 기준이 바뀌는 전환점이 될 가능성이 큽니다.
https://www.biorxiv.org/content/10.1101/2025.11.24.690106v1.full
